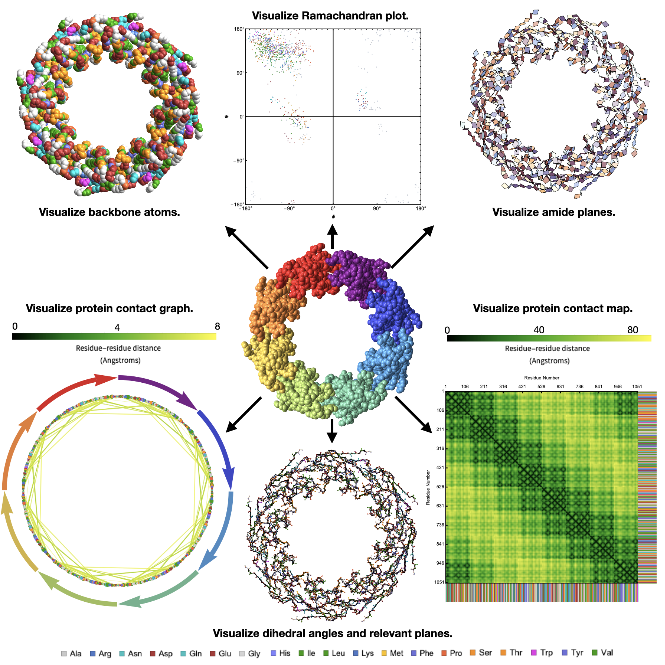
Présentation du paquet ProteinVisualization de Wolfram !
Présentation du paquet ProteinVisualization de Wolfram !
Par Soutick Saha
Introduction
Introduction
Présentation du paquet ProteinVisualization de Wolfram ! Plongez dans le monde fascinant des structures biomoléculaires grâce à cet outil de pointe. Conçu pour les chercheurs, les enseignants et les passionnés de biologie structurale, notre paquet offre une expérience immersive pour visualiser les structures complexes des biomolécules, y compris les protéines, les acides nucléiques et leurs complexes. Explorez l’élégante géométrie des squelettes moléculaires, des plans amide et bien plus encore grâce à des graphiques 3D captivants. Approfondissez votre exploration du monde de la biologie structurale en calculant et en visualisant des caractéristiques clés telles que les cartes de contact et les angles dièdres. Que vous analysez des structures protéiques, étudiez les interactions des acides nucléiques ou admirez simplement la beauté des machines moléculaires de la nature, notre paquet vous permet de voir les biomolécules sous un nouveau jour. Découvrez les merveilles de la visualisation biomoléculaire. Commencez dès aujourd’hui avec notre paquet !
Voici quelques exemples vous montrant comment vous pouvez utiliser différentes fonctions du paquet afin de visualiser de nombreux aspects de la structure des protéines.
Voici quelques exemples vous montrant comment vous pouvez utiliser différentes fonctions du paquet afin de visualiser de nombreux aspects de la structure des protéines.
Visualisations avec le paquet
Visualisations avec le paquet
Installation du paquet
Installation du paquet
Pour installer ce paquet dans votre environnement Wolfram Language, évaluez ce code :
In[]:=
PacletInstall["WolframChemistry/ProteinVisualization"]
Out[]=
Pour charger le code après l’installation, évaluez ce code :
In[]:=
Needs["WolframChemistry`ProteinVisualization`"]
ProteinBackboneAtomPlot
ProteinBackboneAtomPlot
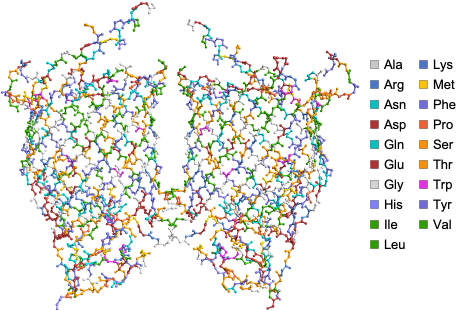
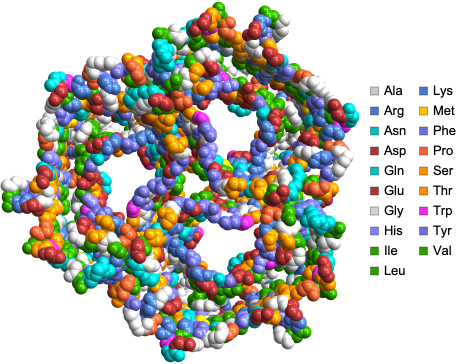
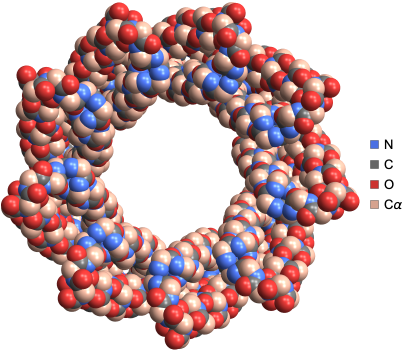
ProteinBackboneAtomPlot génère un tracé 3D, que vous pouvez personnaliser, représentant les atomes et les liaisons du squelette principal d’une protéine ou d’un complexe protéine–acide nucléique, avec des options permettant d’inclure les chaînes latérales, d’afficher des informations sur les résidus ou les atomes, et de coder par couleur les chaînes, les atomes ou les résidus pour une visualisation améliorée.
Visualisez la structure de la protéine à tonneau bêta BamA de E.coli où les atomes sont codés par couleur selon les acides aminés en utilisant la fonction ProteinBackboneAtomPlot :
In[]:=
ProteinBackboneAtomPlot["6FSU"]
Out[]=
Les Options de la fonction ProteinBackboneAtomPlot permettent aux utilisateurs de définir différents thèmes de tracé (PlotThemes) et de colorer les résidus par acides aminés, chaînes ou atomes, et de faire bien plus encore. (Pour voir la liste complète des options, visitez https://resources.wolframcloud.com/PacletRepository/resources/WolframChemistry/ProteinVisualization/ref/ProteinBackboneAtomPlot.html).
Nous pouvons visualiser la structure de la porine spécifique au saccharose ScrY de Salmonella typhimurium en utilisant le PlotTheme « SpaceFilling » :
In[]:=
ProteinBackboneAtomPlot["1A0S",PlotTheme->"SpaceFilling"]
Out[]=
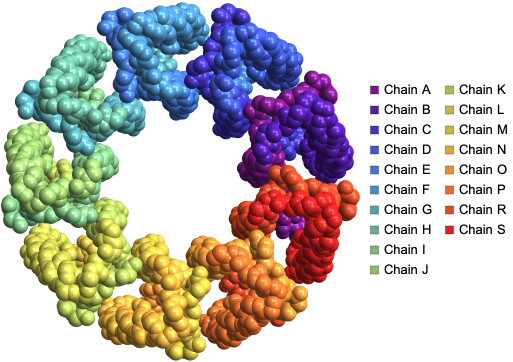
Nous pouvons visualiser la structure de LH2 de Rps. acidophila en utilisant un codage couleur des atomes par chaînes grâce à l’option « BackboneColorRules » :
In[]:=
ProteinBackboneAtomPlot["2FKW",PlotTheme->"SpaceFilling","BackboneColorRules"->{"Chains",Automatic}]
Out[]=
Nous pouvons visualiser la structure d’un toroïde alpha/alpha droitier monocaténaire conçu par calcul comportant 9 répétitions en utilisant un codage couleur des atomes selon leur type d’atome et en spécifiant une couleur pour l’atome α-Carbon :
In[]:=
ProteinBackboneAtomPlot"6XR1",PlotTheme->"SpaceFilling","BackboneColorRules"->"Atoms","Cα"->
Out[]=
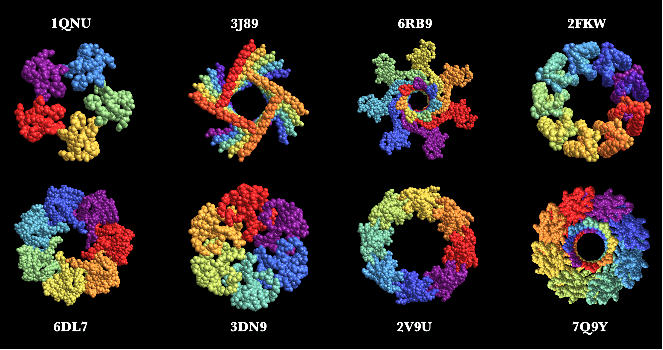
Voici quelques exemples remarquables représentant les structures de protéines avec leurs identifiants PDB à quatre lettres, créés à l’aide de la fonction ProteinBackboneAtomPlot, où les protéines sont codées par couleur selon les chaînes :
AmidePlanePlot
AmidePlanePlot
AmidePlanePlot génère une visualisation 3D des plans amides ainsi que des atomes de la chaîne principale dans une protéine ou un complexe protéine–acide nucléique, mettant en évidence la géométrie plane des liaisons peptidiques. Cela peut constituer un excellent outil pour les enseignants afin d’expliquer aux étudiants des concepts complexes de biologie structurale, lorsqu’il est combiné avec les options de ProteinBackboneAtomPlot.
Voici la visualisation des plans amide pour la structure cristalline de l’insuline, avec cinq atomes de résidus adjacents situés dans le même plan amide :
Il est également possible de ne visualiser que les plans amides des protéines en utilisant l’option « BackboneAtoms ». Voici un exemple de visualisation des seuls plans amides de l’apolipoprotéine humaine A-I tronquée :
Voici quelques exemples intéressants montrant uniquement les plans amide des structures protéiques avec leurs identifiants PDB à quatre lettres créés à l’aide de la fonction AmidePlanePlot :
DihedralAnglePlot
DihedralAnglePlot
DihedralAnglePlot génère une visualisation 3D des squelettes protéiques, mettant en évidence les plans qui forment les angles dièdres ϕ et ψ, et fournit des informations interactives sur les résidus ainsi que les valeurs des angles dièdres lors du survol de la souris. Il s’agit d’un autre excellent outil de visualisation spécialement conçu pour les enseignants afin d’expliquer ce qui donne naissance aux angles dièdres, un aspect complexe mais extrêmement important de la structure des protéines. Cette fonction peut être combinée avec la fonction RamachandranPlot afin d’obtenir une compréhension globale des contraintes portant sur les paires d’angles dièdres possibles autorisées ({ϕ, ψ}) dans les protéines.
Voici le tracé des angles dièdres pour la structure cristalline de la crambine :
Voici quelques exemples intéressants de squelettes protéiques ainsi que des plans qui forment les angles dièdres ϕ et ψ, avec leurs identifiants PDB à quatre lettres, créés à l’aide de la fonction DihedralAnglePlot où les protéines sont codées par couleur selon les résidus d’acides aminés :
ProteinContactMap
ProteinContactMap
ProteinContactMap crée une carte de contacts personnalisable pour une protéine, un acide nucléique ou un complexe protéine–acide nucléique, affichant les interactions résidu–résidu, avec des options permettant de définir la distance seuil des interactions, d’afficher les informations de séquence, de définir des schémas de couleurs et bien plus encore. Vous pouvez utiliser cette fonction, combinée à ses options, pour comprendre les signatures géométriques de différentes classes classiques de structures protéiques telles que le tonneau bêta, la superhélice, et ainsi de suite.
Voici une visualisation de la carte de contact des distances entre résidus dans la structure cristalline du complexe protéine-ARN :
Les options de ProteinContactMap permettent aux utilisateurs de définir la distance de coupure entre les paires de résidus, d’afficher la séquence de la biomolécule avec la carte de contacts, et plus encore. (Pour voir la liste complète des options, visitez https://resources.wolframcloud.com/PacletRepository/resources/WolframChemistry/ProteinVisualization/ref/ProteinContactMap.html).
Voici une visualisation de la carte de contacts des distances entre résidus dans un « CutOff » donné de la structure cristalline du domaine périphérique de la porine principale de Mycobacteria smegmatis :
Dans son utilisation de base, le tracé n’est qu’une signature géométrique de la forme du squelette principal, mais il est possible de créer une empreinte unique d’une protéine en affichant les informations de séquence ainsi que la carte de contacts. Voici un exemple de la carte de contacts des distances entre résidus ainsi que de la séquence de la biomolécule dans la structure cristalline de AChBP provenant de Bulinus truncatus :
Voici quelques exemples intéressants de cartes de contact de protéines avec leurs identifiants PDB à quatre lettres, créées à l’aide de la fonction ProteinContactMap :
ProteinContactGraphPlot
ProteinContactGraphPlot
ProteinContactGraphPlot génère un graphe circulaire des résidus d’une protéine ou d’un complexe protéine–acide nucléique. Dans ce graphe, les nœuds représentent les résidus et les arêtes représentent les interactions dans une distance « CutOff » personnalisable. Les nœuds et les arêtes sont codés par couleur selon le type de résidu et la distance d’interaction, et des options permettent de mettre en évidence des interactions spécifiques, d’ajuster la taille des nœuds, et plus encore.
Cette fonction fournit une version de ResidueDistanceGraph, plus riche en informations, qui génère un graphe non orienté reliant les nœuds proches (résidus de la biomolécule) avec des arêtes monochromes. Alors que ResidueDistanceGraph donne une idée de la topologie globale de la structure protéique sans aucun détail sur des résidus spécifiques ni sur la distance entre les résidus, ProteinContactGraphPlot offre des informations plus détaillées.
Dans ProteinContactGraphPlot, les nœuds (résidus de la biomolécule) sont disposés selon une forme circulaire dans le sens des aiguilles d’une montre. Des infobulles fournissent des informations sur chaque résidu, notamment le nom de la chaîne, le nom de l’acide aminé ou de l’acide nucléique, ainsi que le numéro du résidu. Les informations sur les chaînes sont fournies au moyen de flèches de couleurs distinctes, où la longueur de la chaîne est proportionnelle à la longueur de la flèche. La direction de la flèche suit la directionnalité typique en biologie moléculaire. (Consultez https://fr.wikipedia.org/wiki/Sens_5%27_vers_3%27 [biologie moléculaire]).
Cette fonction fournit une version de ResidueDistanceGraph, plus riche en informations, qui génère un graphe non orienté reliant les nœuds proches (résidus de la biomolécule) avec des arêtes monochromes. Alors que ResidueDistanceGraph donne une idée de la topologie globale de la structure protéique sans aucun détail sur des résidus spécifiques ni sur la distance entre les résidus, ProteinContactGraphPlot offre des informations plus détaillées.
Dans ProteinContactGraphPlot, les nœuds (résidus de la biomolécule) sont disposés selon une forme circulaire dans le sens des aiguilles d’une montre. Des infobulles fournissent des informations sur chaque résidu, notamment le nom de la chaîne, le nom de l’acide aminé ou de l’acide nucléique, ainsi que le numéro du résidu. Les informations sur les chaînes sont fournies au moyen de flèches de couleurs distinctes, où la longueur de la chaîne est proportionnelle à la longueur de la flèche. La direction de la flèche suit la directionnalité typique en biologie moléculaire. (Consultez https://fr.wikipedia.org/wiki/Sens_5%27_vers_3%27 [biologie moléculaire]).
La fonction ProteinContactGraphPlot inclut des options qui permettent aux utilisateurs de définir la distance de coupure entre des paires de résidus, de définir la taille d’un sommet en fonction de sa connectivité, et plus encore .(Pour obtenir une liste complète des options, visitez https://resources.wolframcloud.com/PacletRepository/resources/WolframChemistry/ProteinVisualization/ref/ProteinContactGraphPlot.html). Ces options peuvent être utilisées pour identifier des résidus importants dans la biomolécule.
Voici le graphe des distances de la structure cristalline de la particule centrale du nucléosome avec une taille de sommet mise à l’échelle en fonction de sa connectivité :
Voici quelques exemples intéressants de graphes de contact de protéines/complexes protéine–acide nucléique avec leurs identifiants PDB à quatre lettres créés à l’aide de la fonction ProteinContactGraphPlot :
RamachandranPlot
RamachandranPlot
RamachandranPlot trace les angles dièdres ϕ et ψ d’une protéine ou d’un complexe protéine-acide nucléique. (Consultez https://fr.wikipedia.org/wiki/Diagramme_de_Ramachandran).
Voici le diagramme de Ramachandran de l’hémoglobine humaine désoxygénée :
Les options de la fonction RamachandranPlot permettent aux utilisateurs de définir des couleurs personnalisées pour des résidus individuels, d’obtenir les angles dièdres pour des acides aminés spécifiques et bien plus encore. (Pour obtenir la liste complète des options, visitez https://resources.wolframcloud.com/PacletRepository/resources/WolframChemistry/ProteinVisualization/ref/RamachandranPlot.html).
Voici le diagramme de Ramachandran de la ClpP mitochondriale humaine en complexe avec ONC201 :
Remerciements
Remerciements
Je tiens à remercier Jason Biggs de m’avoir guidé dans le développement et l’amélioration de ce paquet, ainsi que les membres de l’équipe Wolfram Alpha sur la chimie pour leurs retours et suggestions utiles.
CITER CE NOTEBOOK
CITER CE NOTEBOOK
Présentation du paquet ProteinVisualization de Wolfram !
par Soutick Saha
Communauté Wolfram, CHOIX DE L’ÉQUIPE, 31 mai 2023
https://community.wolfram.com/groups/-/m/t/2927764
par Soutick Saha
Communauté Wolfram, CHOIX DE L’ÉQUIPE, 31 mai 2023
https://community.wolfram.com/groups/-/m/t/2927764